精制方法窥视癌细胞内解锁interactome工作
很长一段时间,癌症遗传学和表观遗传学研究人员一直在关注中基因和蛋白质的变化理解是什么让一个细胞癌变,成为恶性。在细胞的细胞核,有高度复杂的基因网络之间的串扰,由小型分散的监管控制元素通过DNA区域的身体接触。
许多癌症显示这相声由于改变,例如,DNA收益,损失或重组。虽然基因可能非常好,是在一个不同的位置在细胞核破坏他们的身体接触能力监管元素。这个网络的交互的研究,被称为interactome,是最具挑战性的和未知的领域之一癌症生物学。
分析interactome不是一项容易的任务。在仔细提取癌细胞的DNA,采取一切可能的预防措施避免干扰的部分基因组“交谈”,科学家把它们一起使用一些生化技巧来揭示哪些基因和监管元素在身体接触。通过比较健康的细胞癌症细胞,研究人员希望了解恶性肿瘤的异常的“话语”。
到目前为止,这种方法需要大量的DNA成功,因此,没有有用的在临床设置由于活检获得的有限的样本大小。但这可能会改变由于liCHi-C-a新方法开发的3 d染色质组织实验室Biola m . Javierre博士领导的约瑟卡雷拉斯白血病研究所,
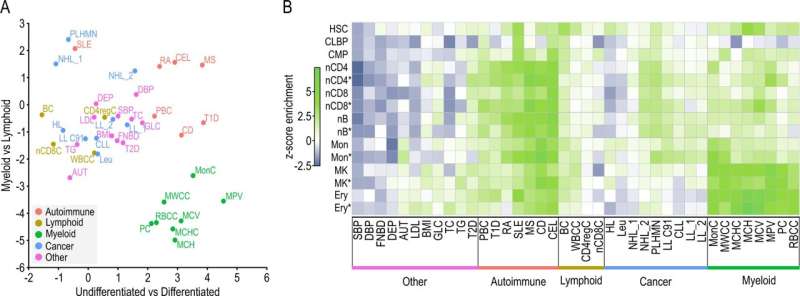
在最近的一份出版物自然通讯研究人员表明,特定肿瘤的interactome可以直接从患者样本进行分析,而不是从体外模型,这是一个大跃进。这一壮举liCHi-C依赖于事实,改善过去启动子捕获高c (PCHi-C)方法,使用只有50000个细胞,而不是其他方法所需的数百万。样本容量的大幅削减可能由于流线型的组合实验协议与新生物信息学工具。
约瑟卡雷拉斯研究所的同事们一起,巴塞罗那超级计算中心,Wellcome-MRC剑桥大学干细胞研究所,桑特琼德德吴IDIBAPS和医院诊所等,研究人员已经能够在发展中增加interactome地图的分辨率造血干细胞从健康的捐赠者和癌症患者,使他们能够识别网络,在白血病发生改变。同时,他们展示liCHi-C可以用来识别精度和较高的大型DNA重组揭示非编码变更在癌症发展的作用。
了解癌症细胞的异常的相声可能帮助开发新的疗法,旨在破坏里面的“有毒喋喋不休”。我们仍然远离诊所,但liCHi-C的第一步是一个更广泛和更丰富的描述发生了什么在癌细胞中,生物医学研究的目标之一。bob88体育平台登录
更多信息:Laureano Tomas-Daza et al,低输入捕捉高分辨率,高c (liCHi-C)标识promoter-enhancer交互自然通讯(2023)。DOI: 10.1038 / s41467 - 023 - 35911 - 8